Сначала отрезаем адаптеры.
java -jar /nfs/srv/databases/ngs/suvorova/trimmomatic/trimmomatic-0.30.jar SE -phred33 SRR4240359.fastq adapters_removed.fastq ILLUMINACLIP:adapters.fasta:2:7:7 TrimmomaticSE: Started with arguments: -phred33 SRR4240359.fastq adapters_removed.fastq ILLUMINACLIP:adapters.fasta:2:7:7Реузльтат: Input Reads: 13557938 Surviving: 13502066 (99,59%) Dropped: 55872 (0,41%)
Размер файла со чтениями до: 1375Мб, после: 1369Мб.
Затем очистка чтений.
java -jar /nfs/srv/databases/ngs/suvorova/trimmomatic/trimmomatic-0.30.jar SE -phred33 adapters_removed.fastq trimmed.fastq TRAILING:20 MINLEN:32Результат: Input Reads: 13502066 Surviving: 12184080 (90,24%) Dropped: 1317986 (9,76%)
Размер файла со чтениями до: 1369Мб, после: 1223Мб.
Команда: velveth velveth 31 -short -fastq trimmed.fastq
Программа принимает на вход очищенные от адаптеров и фильтрованные чтения и создает в текущей директории несколько файлов: Roadmap, Log, Sequences. Суть работы программы заключается в создании хэш таблиц с k-мерами.
Команда: velvetg velveth
N50= 70607
| № | Длина | Покрытие |
|---|---|---|
| 1 | 108447 | 42.009186 |
| 11 | 125674 | 44.550949 |
| 13 | 71403 | 39.411551 |
| ID | Число гэпов | Identity | Query Cover | Score |
| 1 | 556/13014(4%) | 74.96% | 10% | 5465 |
| 11 | 126/9631(1%) | 82.85% | 14% | 8517 |
| 13 | 195/7059(2%) | 80.22% | 9% | 5121 |
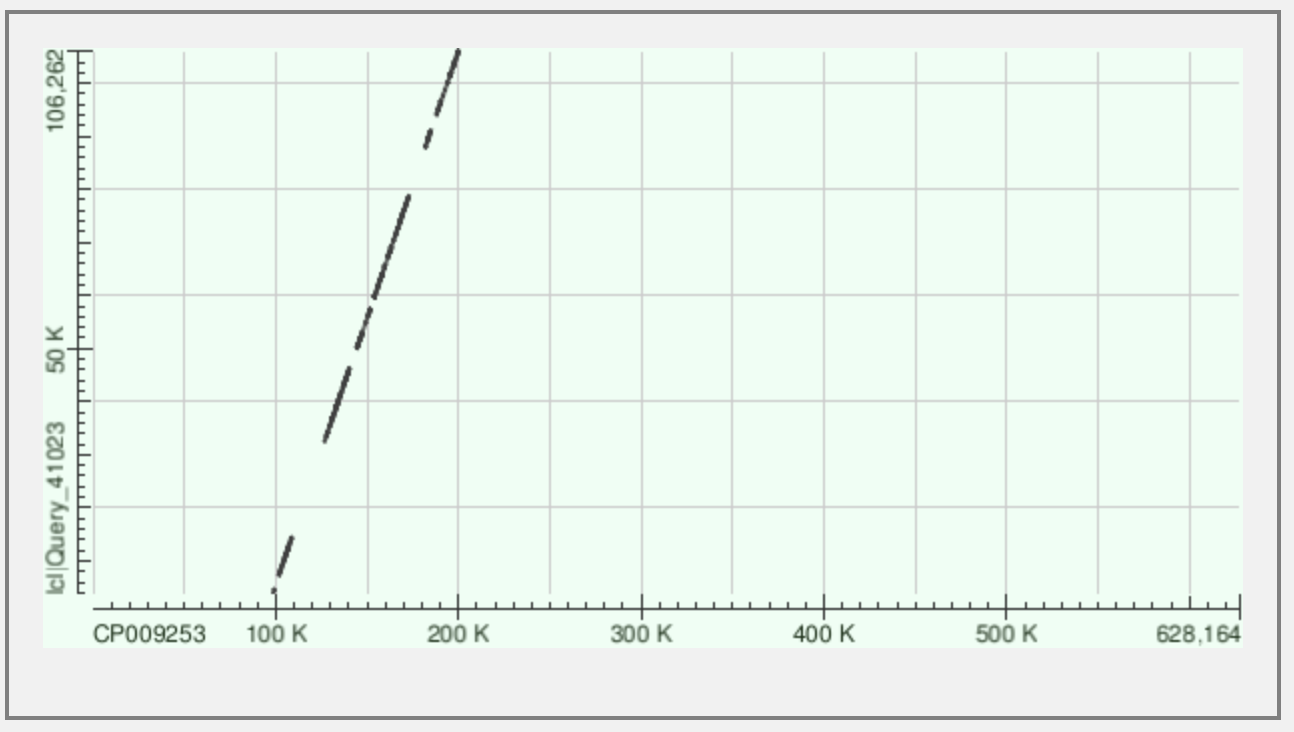
Для контига 1: одинаковое направление с хромосомой


Для контига 11: проходит через нулевую координату
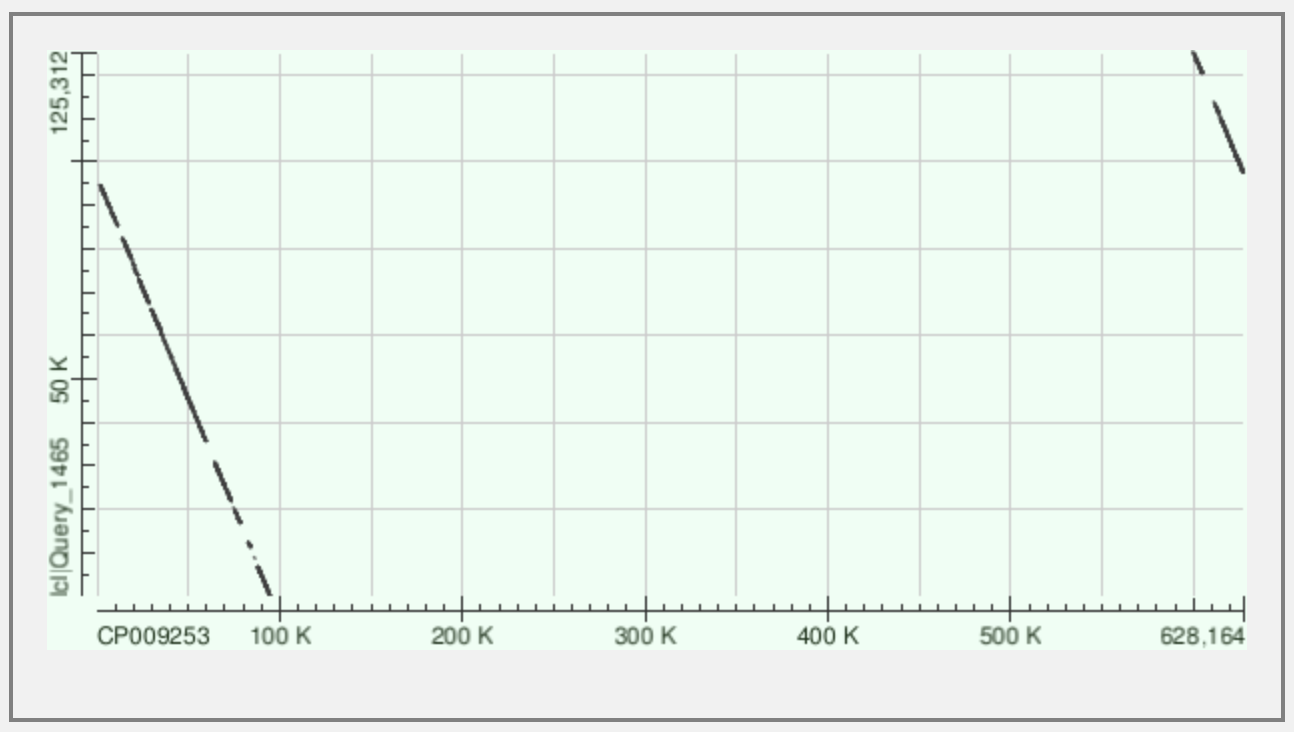

Для контига 13: имеет обратное направление
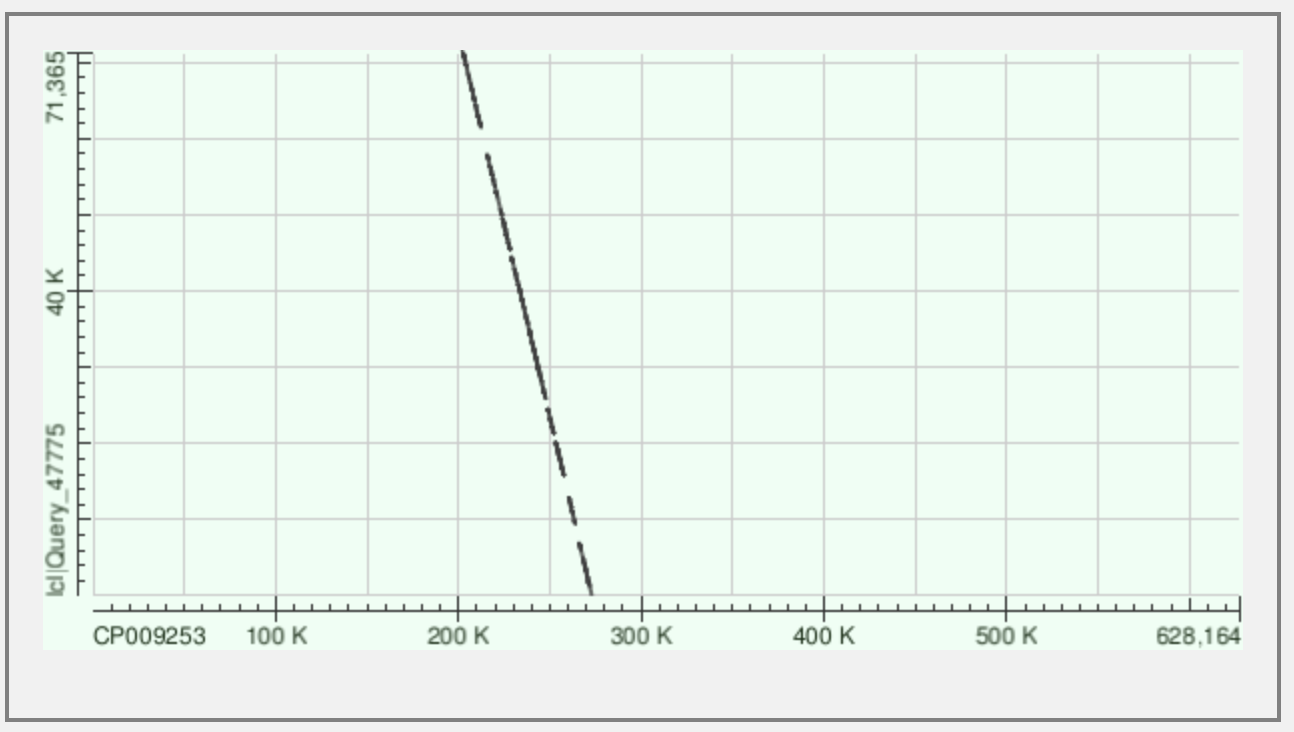

Можно сказать, что в целом контиги занимают достаточно большую часть генома.